GlaI-ПЦР анализ метилирования сайта ACGC в хp11: 65647266 в препаратах ДНК клеток крови в норме и на ранних стадиях рака молочной железы
А.Г. Акишев1 *, Н.А. Нетесова2, М.А. Абдурашитов1, И.В. Вихлянов3, М.К. Никитин3, А.Б. Карпов4, С.Х. Дегтярев1
1 НПО «СибЭнзим» Новосибирск
2 ООО «Эпигенлаб» Новосибирск
3 КГБУЗ «Алтайский краевой онкологический диспансер», 656049, Алтайский край, г. Барнаул
4 ФГУП Северский биофизический научный центр ФМБА России, г. Северск, Томская область
* автор для переписки: Александр Акишев, НПО СибЭнзим, ул. Тимакова, д. 2/12 , Новосибирск, 630117, Россия; тел.: +7(383)333-4991; факс: +7(383)333-6853; E-mail: aki@sibenzyme.ru
Методом GlaI-ПЦР анализа изучали метилирование сайта ACGC в гене SIPA1 в положении хр11: 65647266 (согласно базе данных GRCh38 PrimaryAssembly) в препаратах ДНК, полученных из легкой фракции клеток крови доноров и больных раком молочной железы на ранних стадиях заболевания. Исследование включало а) получение легкой фракции клеток крови, б) выделение геномной ДНК, в) установление методом ПЦР в реальном времени концентрации геномной ДНК, г) определение методом GlaI-ПЦР-анализа концентрации неметилировнного сайта ACGC в положении хр11: 65647266 в препаратах ДНК из легкой фракции клеток крови и д) определение доли молекул ДНК, содержащих неметилированный сайт ACGC, выраженной в процентах от общего количества молекул ДНК.
GlaI-ПЦР анализ показал, что у более чем 82% доноров доля неметилированного сайта ACGC в положении хр11: 65647266 в ДНК из легкой фракции клеток крови составляет 3% и менее, тогда как у приблизительно 70% больных РМЖ процент неметилированного сайта ACGC выше и находится в диапазоне от 3,2 до 6,4%. Эти данные позволяют предположить, что при РМЖ на ранних стадиях у 2/3 больных в ДНК небольшой части лейкоцитов (до 3,5%) происходит деметилирование сайта A(5mC)GC в гене SIPA1 в положении 65647266.
Данные, представленные в данной работе, могут быть использованы для разработки ПЦР тест-системы, позволяющей исключить РМЖ на ранних стадиях. Метод GlaI-ПЦР анализа не требует сложного и дорогостоящего оборудования и реактивов, а само исследование может проводиться в стандартной ПЦР-лаборатории в ходе ежегодных профилактических обследований и анализа крови.
Ключевые слова: рак молочной железы (РМЖ), метилирование ДНК, GlaI-ПЦР анализ
DOI: 10.26213/SE.2019.66.12.001
Данные для цитирования:
Акишев А.Г. , Нетесова Н.А., Абдурашитов М.А., Вихлянов И.В., Никитин М.К., Карпов А.Б., Дегтярев С.Х. (2019) GlaI-ПЦР анализ метилирования сайта ACGC в хp11: 65647266 в препаратах ДНК клеток крови в норме и на ранних стадиях рака молочной железы, Эпигенетич ДНК диагност, том 2019(1), DOI: 10.26213/SE.2019.66.12.001

Эта статья доступна по лицензии Creative Commons Attribution-NonCommercial-NoDerivatives 4.0 International
Введение
Рак молочной железы (РМЖ) является наиболее распространенным онкологическим заболеванием у женщин. По статистическим данным, каждая десятая женщина сталкивается с этой болезнью. Число ежегодно выявляемых случаев РМЖ в мире по данным Всемирной Организации Здравоохранения достигает 1,38 млн., а число смертей от РМЖ — 460 тыс. [1, 2]. Одной из главных причин высокой смертности является позднее обнаружение заболевания. Это вызвано тем, что существующие методы диагностики РМЖ (пальпация, маммография, томография, УЗИ и т.д.) не способны обнаруживать опухоли небольшого размера, зачастую расположенные в глубине ткани молочной железы. В связи с этим существует насущная необходимость разработки методов ранней диагностики РМЖ, позволяющих определять наличие заболевания на ранних стадиях.
В настоящее время одним из наиболее перспективных направлений диагностики онкологических заболеваний является эпигенетическая ДНК-диагностика, в частности, определение в препаратах ДНК крови статуса метилирования некоторых цитозиновых оснований в регуляторных элементах генов. При образовании опухоли статус метилирования этих цитозинов меняется, это изменение может быть как деметилированием 5-метилцитозина, так и метилированием цитозина. Процесс изменения статуса метилирования происходит на ранних стадиях заболевания [3,4] и делает этот признак особенно ценным с точки зрения диагностического потенциала.
Метилирование ДНК de novo, включая аберрантное гиперметилирование, осуществляется ДНК-метилтрансферазами Dnmt3a и Dnmt3b, которые узнают преимущественно сайт RCGY и модифицируют внутренний CG-динуклеотид с образованием последовательности R(5mC)GY в обеих цепях ДНК [5], где R – A или G, Y – T или C, 5mC – 5-метилцитозин. В дальнейшем метилирование модифицированных сайтов поддерживается в ходе репликации ДНК-метилтрансферазой Dnmt1. Метилзависимая сайт-специфическая ДНК-эндонуклеаза GlaI узнает и расщепляет (как указано стрелкой) именно сайт R(5mC)¯GY [6], что делает ее удобным инструментом для выявления неметилированных сайтов RCGY в ДНК человека. На основе фермента GlaI нами был разработан метод GlaI-ПЦР анализа в реальном времени, позволяющий выявлять наличие молекул ДНК с неметилированным сайтом RCGY, расположенными внутри изучаемого фрагмента генома человека [7]. GlaI-ПЦР анализ проводится в два этапа и включает а) гидролиз ДНК ферментом GlaI и б) проведение ПЦР в реальном времени с геномных праймеров, окаймляющих анализируемый сайт RCGY. Использование флуоресцентно-меченого зонда, комплементарного участку ДНК между геномными праймерами, существенно повышает специфичность ПЦР в реальном времени.
GlaI-ПЦР анализ показал, что у более чем 82% доноров доля неметилированного сайта ACGC в положении хр11: 65647266 в ДНК из легкой фракции клеток крови составляет 3% и менее, тогда как у приблизительно 70% больных РМЖ процент неметилированного сайта ACGC выше и находится в диапазоне от 3,2 до 6,4%. Эти данные позволяют предположить, что при РМЖ на ранних стадиях у 2/3 больных в ДНК небольшой части лейкоцитов (до 3,5%) происходит деметилирование сайта A(5mC)GC в гене SIPA1 в положении 65647266.
Полученные данные могут быть использованы для разработки ПЦР тест-системы, позволяющей исключить диагноз «РМЖ на ранних стадиях» и включающей: а) проведение ПЦР в реальном времени для определения молярной концентрации препарата ДНК [7] из легкой фракции клеток крови [8], б) GlaI-ПЦР анализ для установления концентрации неметилированного сайта ACGC в 11-ой хромосоме в положении 65647266, в) установление доли неметилированного сайта в анализируемом препарате ДНК.
Материалы и методы
Материалы
В работе использовали бидистиллированную воду, физиологический раствор для инъекций (ООО «Красфарма», Красноярск), фенол (ОАО «Реактив», Новосибирск), хлороформ (ОАО «Реактив», Новосибирск), изоамиловый спирт (ОАО «Реактив», Новосибирск), РНКаза А (ООО «Самсон-Мед», Санкт-Петербург), SDS (ООО «Хеликон», Москва). Набор для проведения GlaI-ПЦР анализа, набор для очистки ДНК из легкой фракции клеток крови, ДНК клеточных линий Raji и U-937, ДНК фага лямбда, рестриктазы TaqI, VspI, MspI и буферные растворы производства НПО «СибЭнзим». В контрольных экспериментах использовали геномную ДНК из печени мышей-самцов линии A/He в возрасте 5-6 месяцев, которая выделялась, как описано ранее [9]. VspI-гидролизат ДНК клеточной линии человека Raji получали расщеплением 10 мкг ДНК Raji рестриктазой VspI в 300 мкл буфера W при 37ºС в течение 1 часа с последующей очисткой ДНК как описано ранее [9].
Материалом для исследования служили образцы ДНК, выделенные из легкой фракции клеток крови 19 больных РМЖ и 28 условно здоровых доноров. Получение легкой фракции клеток крови и выделение из нее ДНК проводили с использованием набора для очистки ДНК из легкой фракции клеток крови как описано в протоколе компании-производителя [8] с некоторыми модификациями.
Методы
Взятие периферической крови проводили утром натощак из кубитальной вены. При заборе крови использовали иглы «Vacuette», 38 х 0,8 мм, 21Gх11/2 и пробирки «Vacuette» на 9 мл с ЭДТА (EDTA K2 или EDTA K3). Вакутейнер с кровью (непосредственно после забора) осторожно переворачивали 7-8 раз и центрифугировали 3 мин при 1000 g на центрифуге ELMI CM-6MT (Латвия).
Из каждого вакутейнера пипеткой на 1 мл с обрезанным наконечником (с фильтром) осторожно отбирали всю плазму, стараясь избежать взмучивания осадка клеток крови и захвата эритроцитов, в градуированную пробирку на 15 мл. Пробирки уравновешивали попарно физраствором и центрифугировали 10 минут при 1000g (ELMI). Супернатант отбирали пипеткой и отбрасывали. К осадку добавляли 3 мл физраствора и, используя пипетку с обрезанным наконечником, аккуратно суспендировали осадок. В каждую пробирку добавляли еще по 10 мл физраствора, содержимое пробирок аккуратно перемешивали переворачиванием и центрифугировали 10 минут при 1000g (ELMI). Супернатант декантировали, а остатки супернатанта отбирали пипеткой и отбрасывали. Полученный осадок клеток хранили при —20ºС. Выделение ДНК из осадка проводили, как описано ниже, либо сразу после его получения, либо после хранения при —20ºС.
Выделение ДНК из осадка проводили с использованием набора для выделения ДНК из легкой фракции клеток крови К008S (СибЭнзайм) согласно протоколу производителя [7]. К осадку в пробирке добавляли 1,6 мл раствора №1 и пипетированием суспендировали осадок до мелких частиц в течение 1-2 минут. Из полученной суспензии (~ 1,7 мл) отбирали по 850 мкл в 2 пробирки на 2 мл, помещали их на 30 мин в термостат при 55ºС, время от времени перемешивая содержимое пробирок переворачиванием, чтобы полностью растворить мелкие частицы. Затем в каждую пробирку добавляли по 300 мкл раствора №2, перемешивали содержимое пробирок переворачиванием 2-3 раза и помещали пробирки на 7 минут в морозильную камеру при —20ºС. После чего центрифугировали пробирки 7 минут при 13000 об/мин (Eppendorf).
Супернатант из пробирок (~1 мл) переносили, соответственно, в две новые пробирки на 2 мл, добавляли туда по 900 мкл раствора №3, перемешивали смесь переворачиванием пробирок 3 раза и центрифугировали пробирки в течение 5 минут при 13000 об/мин (Eppendorf). Супернатант аккуратно отбирали пипеткой и отбрасывали.
Промывали осадок добавлением 500 мкл 70%-ного этанола и переворачиванием пробирок 3-4 раза. Центрифугировали 1 минуту при 13000 об/мин (Eppendorf). Супернатант аккуратно отбирали пипеткой (по возможности, не оставляя жидкости в пробирке) и отбрасывали. Повторно промывали осадок 500 мкл 70%-ного этанола (см. выше). Помещали открытые пробирки на рабочий стол на 10-15 минут для подсушивания осадка (до исчезновения влаги). Осадки в 2-х пробирках последовательно растворяли в смеси из 450 мкл воды и 10 мкл TE-буфера. К полученному раствору ДНК добавляли 55 мкл SE-буфера Y(х10), 2 мкл рестриктазы TaqI и 3 мкл РНКазы А (10 мг/мл). Перемешивали переворачиванием и выдерживали 40 минут в термостате при 65ºС.
После окончания инкубации проводили фенол-хлороформную очистку как описано ранее [9]. В пробирки добавляли равный объем фенола, насыщенного 10 mM Трис-HCl (pH = 8,0). Содержимое пробирок интенсивно перемешивали, затем центрифугировали при 12000 об/мин 3 минуты. Верхнюю (водную) фазу переносили в новую пробирку на 2 мл, не захватывая интерфазы. К водной фазе добавляли равный объем смеси «фенол : хлороформ : изоамиловый спирт» (в соотношении 25 : 24 : 1). Интенсивно перемешивали содержимое пробирок, затем центрифугировали в том же режиме. Верхнюю (водную) фазу переносили в новую пробирку на 2 мли к ней добавляли равный объем смеси «хлороформ : изоамиловый спирт» (в соотношении 24 : 1). Интенсивно перемешивали содержимое пробирок, затем центрифугировали в том же режиме. Верхнюю водную фазу переносили в новую пробирку на 2 мл и проводили экстракцию смесью «хлороформ : изоамиловый спирт» еще раз (см. выше).
Водную фазу переносили в пробирку на 2 мл и осаждали ДНК добавлением 0,1 объема 3 M ацетата калия (pH = 7,0) и 2,5 объемов холодного 96 % этанола. Интенсивно перемешивали содержимое пробирок и выдерживали 1 час при -20оС. Центрифугировали пробирки в течение 5 минут при 12000 об/мин. Супернатант аккуратно отбирали пипеткой (по возможности, не оставляя жидкости в пробирке) и отбрасывали. Осадок промывали 300 мкл 70 %-ного водного раствора этанола (как описано выше) два раза, центрифугируя пробирки с осадками в течение 5 минут при 13000 об/мин (Eppendorf). Супернатант аккуратно отбирали пипеткой (по возможности, не оставляя жидкости в пробирке) и отбрасывали. Осадки подсушивали на столе в течение 10-15 минут. Затем осадок растворяли в 400 мкл ТЕ-буфера и определяли его концентрацию на спектрофотометре «NanoVue Plus» (GE Healthcare, Великобритания). В случае высокой концентрации полученных препаратов ДНК (более 30 нг/мкл) их разбавляли ТЕ-буфером до концентрации ДНК приблизительно 30 нг/мкл.
Замороженные осадки легкой фракции клеток крови больных РМЖ были получены от пациентов с различными стадиями заболевания и хранились при -20С. По клинической стадии заболевания пациенты распределялись следующим образом: 12 больных имели стадию заболевания 1а (T1N0M0), 5 больных – стадию 2а (T2N0M0), двое больных – стадию 2б (T2N1M0). У всех доноров биологического материала было получено информированное согласие на участие в исследовании.
Определение концентрации фрагмента гена SIPA1 и сайта ACGC в 11-ой хромосоме в положении 65647266 проводили методом ПЦР в реальном времени в стандартных планшетках на 96 лунок с использованием набора для GlaI-ПЦР анализа («СибЭнзайм»). С помощью данного набора в каждом из исследуемых препаратов ДНК легкой фракции клеток крови определяли концентрацию молекул, содержащих фрагмент 11-й хромосомы в положении 65647215 – 65647307, а также концентрацию неметилированного сайта ACGC в 11-ой хромосоме в положении 65647266. Каждое исследование проводилось в трех повторах – триплетах.
При анализе N препаратов ДНК готовили реакционную смесь для анализа 2хN препаратов ДНК, при этом в реакционную смесь для каждого триплета добавляли по 1 мкл полученного препарата ДНК и 14 мкл воды. В итоге каждая из трех точек в ПЦР содержала около 9 нг ДНК (~3х103 копий гаплоидного хромосомного набора) или меньше в зависимости от концентрации полученного препарата ДНК легкой фракции клеток крови. Стандартно готовили реакционную смесь для анализа 12 препаратов ДНК, представленных в дублях (24 пробирки — 72 лунки в ПЦР), ДНК мыши (3 лунки в ПЦР) и для построения калибровочной прямой (5 пробирок – 15 лунок в ПЦР). Для построения калибровочной прямой использовали VspI-гидролизат ДНК опухолевой клеточной линии человека Raji, концентрацию которой определяли по данным измерения оптической плотности при длине волны 260 нм. Приготовление образцов VspI-гидролизата ДНК клеточной линии человека Raji для построения калибровочной прямой проводили, как описано ниже.
Готовили 5 пробирок с «точками калибровки» и одну контрольную. В пробирку 1 вносили 26 мкл воды, в пробирки 2, 3, 4, 5 – по 15 мкл воды, в пробирку 6 – 14 мкл воды. В пробирку 1 добавляли 4 мкл VspI-гидролизата ДНК Raji в концентрации 18 нг/мкл и перемешивали с последующим сбросом капель центрифугированием. Из пробирки 1 переносили 15 мкл раствора ДНК в пробирку 2 с последующим перемешиванием. Из пробирки 2 переносили 15 мкл раствора ДНК в пробирку 3 с последующим перемешиванием. Из пробирки 3 переносили 15 мкл раствора ДНК в пробирку 4 с последующим перемешиванием. Из пробирки 4 перенесли 15 мкл раствора ДНК в пробирку 5 с последующим перемешиванием. Удаляли 15 мкл смеси из пробирки 5. В пробирку 6 добавляли 1 мкл раствора ДНК печени мыши в концентрации 18 нг/мкл и перемешивали с последующим сбросом капель центрифугированием.
Реакционная смесь А готовилась из компонентов набора для GlaI-ПЦР анализа и содержала (из расчета на 1 триплет) 4.17 мкл воды, 2.28 мкл 10xТМN буфера, 0.03 мкл ДНК фага лямбда (18нг/мкл), 0.23 мкл БСА (10 мг/мл), 0.12 мкл β-меркаптоэтанола (0,2М) и 0.12 мкл эндонуклеазы рестрикции MspI (20ед/мкл).
К препаратам ДНК добавляли по 6,6 мкл реакционной смеси А и инкубировали 30 мин при 37°С с последующим прогревом 15 мин при 65°С. Сбрасывали капли на микроцентрифуге.
Реакционная смесь Б готовилась из компонентов набора для GlaI-ПЦР анализа и содержала (из расчета на 1 триплет) 8.0 мкл воды, 0.85 мкл 10xТМN буфера, 0.01 мкл ДНК фага лямбда (18нг/мкл), 0.09 мкл БСА (10 мг/мл), 0.05 мкл β-меркаптоэтанола (0,2М) и 0.08 мкл MD ДНК-эндонуклеазы (20ед/мкл).
После инкубации с реакционной смесью А и прогрева при 650С (см. выше) в пробирки добавляли по 8,6 мкл реакционной смеси Б и инкубировали 40 мин при 37°С. Сбрасывали капли на микроцентрифуге и добавляли по 30,2 мкл реакционной смеси, содержащей (из расчета на 1 триплет) воды 20.8 мкл, буфер GLADх10 6.3 мкл, БСА (10 мг/мл) 0.6 мкл, dNTP (10 mM каждый) 1.2 мкл, смесь праймеров и зонда (10 µM каждый) 2.4 мкл и SP-Taq ДНК-полимеразу (5 ед/мкл) 0.4 мкл. После перемешивания содержимое каждой пробирки (60 мкл) разносили по 20 мкл в лунки ПЦР-плашки.
Для расчета специфических праймеров и зондов использовали нуклеотидные последовательности из базы данных GenBank (http://ncbi.nlm.nih.gov/genbank) по версии генома человека GRCh38/hg38, семейство программ “Vector NTI 11.5” (Invitrogen, США) и онлайн-ресурс «BLAST» (http://blast.ncbi.nlm.nih.gov). Ниже указана структура праймеров и флуоресцентно меченого зонда, используемых в работе:
SIPA1F 5′ TGG TGC CCT CGG GTA AGC G 3′
SIPA1R 5′ CCC AGG CCA CAC GGA ACT TTC 3′
SIPA1Z 5′ FAM-CCA CCG CCC GAG GGA TGA AGA CC-BHQ1 3’
ПЦР в реальном времени стандартов ДНК клеточной линии Raji и дублей 12-ти образцов ДНК легкой фракции клеток крови проводили согласно протоколу производителя [10] в объеме 20 мкл на детектирующем амплификаторе CXF-96 («Bio-Rad», США) по следующей программе: при 95°C — 3 мин; 5 «слепых» циклов: 95°C — 10 сек, 67°C (с понижением на 0.5°C в каждом последующем цикле — 20 сек, 72°C — 5 сек, 75°C — 5 сек; 40 циклов: 95°C — 10 сек, 64°C — 20 сек (с детекцией флуоресцентного сигнала в канале FAM), 72°C — 5 сек, 75°C — 5 сек.
По завершении ПЦР, при помощи программного обеспечения амплификатора “Bio-Rad CFX Manager v.2.1”, устанавливали количество молекул ДНК с фрагментом гена SIPA1 и количество неметилированных сайтов ACGC, расположенных в 11-ой хромосоме в положении 65647266, в 0,33 мкл исследуемых препаратов ДНК.
Результаты и обсуждение
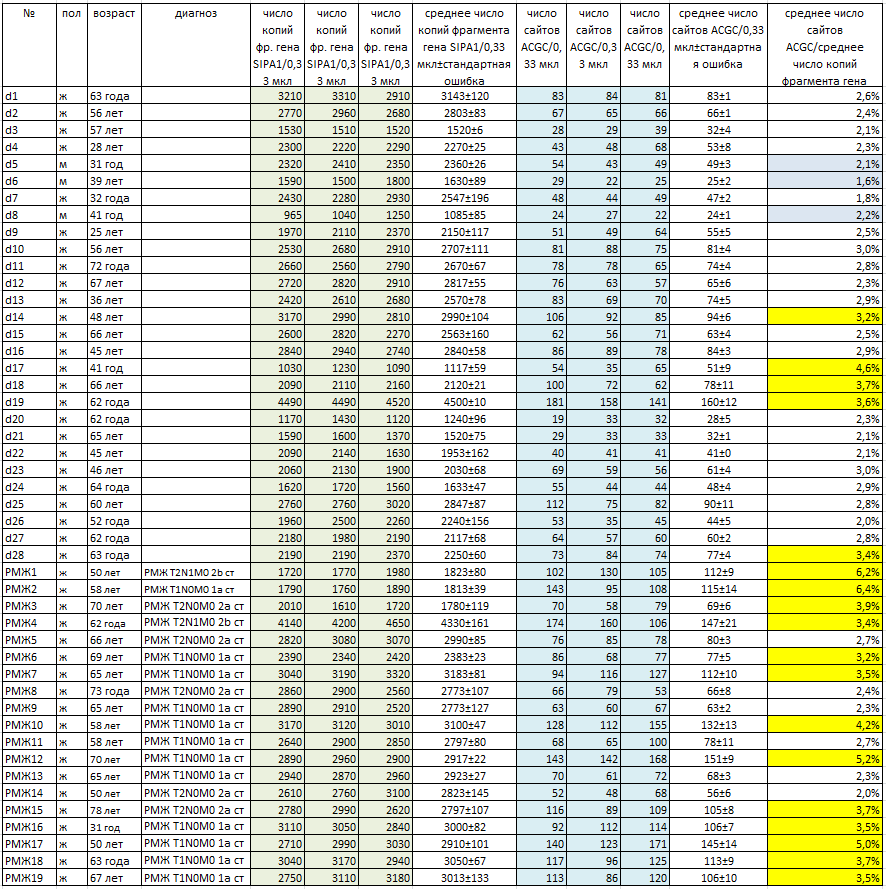
Выделение ДНК из легкой фракции клеток крови доноров и больных РМЖ. Получение легкой фракции клеток крови больных и доноров и последующее выделение ДНК проводили, как описано в «Материалах и Методах». Забор крови проводили утром натощак из вены в вакутейнеры с ЭДТА. ДНК очищали с помощью набора для выделения ДНК из легкой фракции клеток крови согласно инструкции к набору, с некоторыми изменениями как описано в «Материалах и методах». Вся процедура получения клеток и очистки ДНК занимает 5-6 часов. В нашей работе проводилось выделение ДНК из осадков легкой фракции клеток крови от 19 больных РМЖ и 28 условно здоровых доноров. Забор крови проводился только у первичных больных при их поступлении в стационар. Гистологические данные по опухоли (TMN) были получены после хирургической операции. В таблице 1 представлены данные по донорам и больным, включая его номер (столбец 1), пол (столбец 2) и возраст (столбец 3). В столбце 4 указаны TMN данные больных РМЖ. Как видно из таблицы в число доноров входили 25 женщин и трое мужчин в возрасте от 28 до 72 лет. В списке больных РМЖ возраст женщин варьировался от 31 года до 78 лет. При этом, как видно из таблицы, основная часть препаратов ДНК (17 из 19) были получены от больных на ранних стадиях заболевания (до стадии 2б).
Структура исследуемого фрагмента гена SIPA1. Фрагмент ДНК, изучаемый в данной работе, находится в 11-ой хромосоме в районе гена SIPA1 в положении 65647215-65647307. Структура анализируемого фрагмента представлена на рисунке 1, где указаны положения праймеров SIPA1F (желтый цвет) и SIPA1R (коричневый цвет), зонда SIPA1Z (зеленый цвет) и анализируемого сайта метилирования ACGC (красный цвет).
Рисунок 1.
Структура анализируемого фрагмента гена SIPA1

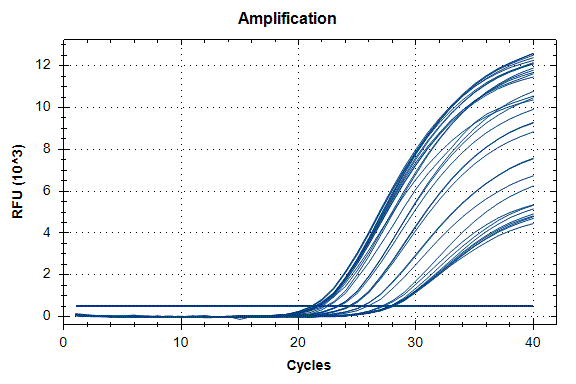
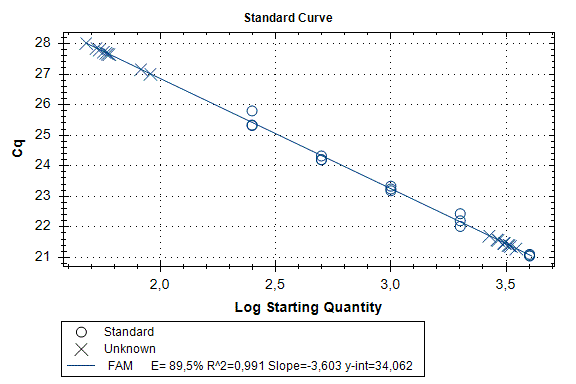
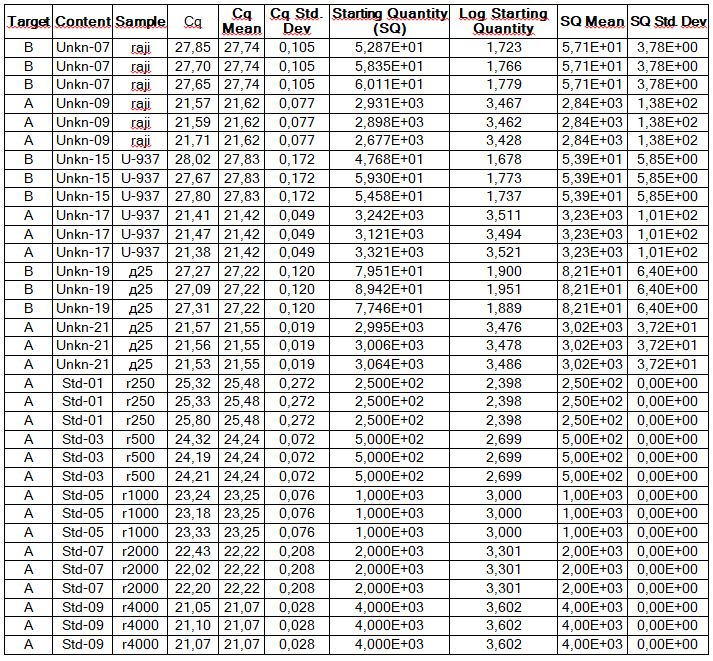
Определение количества копий фрагмента гена SIPA1 в полученных препаратах ДНК легкой фракции клеток крови. На рисунке 2 представлены кривые накопления флуоресценции в ходе ПЦР в режиме реального времени при определении количества копий фрагмента гена SIPA1 в препаратах VspI-гидролизатов ДНК клеточной линии Raji в концентрации 4000, 2000, 1000, 500 и 250 копий/20 мкл реакционной смеси, которые использовались в качестве стандартов в данном эксперименте. На рисунке также представлены кривые накопления флуоресценции для анализируемых препаратов ДНК клеточных линий Raji и U-937, а также донора d25 в концентрации 3000 копий/20 мкл реакционной смеси. Каждый препарат анализировался дважды: с расщеплением по сайту A(5mC)GC и без гидролиза по данному сайту. При этом, как описано в «Материалах и методах» реакции проводились в триплетах и во второй части рисунка представлены полученные значения Cq для каждой точки в триплете. Путем сравнения со значениями Cq, полученными для стандартов, определялось число копий фрагмента гена SIPA1 в каждом эксперименте, а также среднее значение числа копий в триплете. Как видно из представленных результатов число копий фрагмента гена SIPA1 в анализируемых препаратах ДНК донора и клеточных линий составляет около 3000 в 20 мкл, при этом после расщепления по сайту A(5mC)GC число копий фрагмента в препаратах существенно уменьшается и составляет от 1,7 до 2,8%.
Рисунок 2
Пример результатов количественного GlaI-ПЦР анализа препаратов ДНК клеточных линий Raji и U-937, а также донора d25
здесь:
А – Фрагмент ДНК гена SIPA1 в 11-й хромосоме в положении 65647215 – 65647307.
В — Фрагмент ДНК гена SIPA1 в 11-й хромосоме в положении 65647215 – 65647307, расщепленный по сайту A(5mC)GC в положении 65647266.
Таким образом, концентрация анализируемых препаратов ДНК донора и клеточных линий приблизительно одинаковая, а сайт ACGC в гене SIPA1 метилирован более чем на 97%.
В дальнейшем определение количества копий фрагмента гена SIPA1 и числа сайтов ACGC в 0,33 мкл изучаемых препаратов ДНК проводилось в трех экспериментах, для каждого из них реакционная смесь готовилась отдельно. При этом, как описано в «Материалах и методах», в каждом эксперименте реакция проводилась трижды и устанавливалось среднее значение параметра.
В таблице 1 для каждого образца ДНК представлены установленные значения количества копий фрагмента гена SIPA1 (столбцы 5, 6, 7) и число неметилированных сайтов ACGC (столбцы 9, 10, 11) в 0,33 мкл анализируемых препаратов ДНК, полученные методом ПЦР в реальном времени с использованием набора для GlaI-ПЦР анализа.
В столбце 8 и 12 указаны средние значения концентрации фрагмента гена SIPA1 и сайта ACGC, соответственно, для каждого образца с указанием стандартной ошибки определения. Как видно из таблицы 1 полученные средние значения концентрации фрагмента ДНК SIPA1 (и, соответственно, геномной ДНК) варьируют от 1085 (d8) до 4500 (d19) копий в 0,33 мкл. При этом, количество молекул ДНК, содержащих сайт ACGC в 11-ой хромосоме в положении 65647266, варьирует от 24 (d8) до 160 (d19) в 0,33 мкл.
Определение доли молекул ДНК, содержащих неметилированный сайт ACGC в 11-ой хромосоме в положении 65647266. Далее определялось количество молекул ДНК, содержащих сайт ACGC в 11-ой хромосоме в положении 65647266, по отношению к общему числу молекул ДНК в исследуемых препаратах. Эта величина определялась путем деления среднего значения концентрации сайтов ACGC (столбец 12 в таблице 1) на среднее значение числа копий геномной ДНК в 0,33 мкл (столбец 8 в таблице 1). В таблице 1 в столбце 13 представлены полученные значения доли молекул ДНК, содержащих неметилированный сайт ACGC в 11-ой хромосоме в положении 65647266, выраженные в процентах.
Как видно из таблицы, во всех образцах ДНК определяется менее 7% неметилированных сайтов ACGC в гене SIPA1. Таким образом, в препаратах ДНК исследуемых образцов более чем 93% сайтов в гене SIPA1 находятся в метилированной форме A(5mC)GC. Из данных в таблице также видно, что в большинстве препаратов ДНК доноров процент неметилированных сайтов еще ниже (3% и менее), что соответствует данным, представленным на рисунке 2. Процент сайта ACGC в гене SIPA1 у трех доноров-мужчин (d5, d6 и d8) заметно не отличается от данного показателя у женщин и составляет от 1,6 до 2,2.
При этом, у 5-ти из 28 образцов ДНК доноров (менее, чем 18%) уровень метилирования составляет от 3,2 до 4,6%. В тоже время лишь 6 из 19 образцов ДНК больных РМЖ имеют долю неметилированного сайта ACGC в гене SIPA1 на уровне 2,0% — 2,7%, тогда как у остальных 13-ти образцов ДНК больных РМЖ (около 70%) доля неметилированных сайтов составляет от 3,2% до 6,4%. Поскольку легкая фракция клеток крови состоит преимущественно из лейкоцитов, полученные данные позволяют предположить, что у приблизительно 2/3 больных РМЖ на ранних стадиях в ДНК небольшой части лейкоцитов (до 3,5%) происходит деметилирование сайта A(5mC)GC в гене SIPA1 в положении 65647266.
Сайт ACGC в 11-ой хромосоме в положении 65647266 расположен в интроне гена SIPA1 (signal-induced proliferation-associated 1). Согласно базе данных GeneHancer [11] эта позиция находится в зоне энхансера GH11J065646, который содержит сайт связывания фактора транскрипции CTCF. Ранее было показано, что метилирование сайта связывания фактора CTCF приводит к блокировке энхансерной функции этого участка ДНК [12]. По-видимому, у двух третей больных РМЖ на начальных стадиях, в ДНК небольшой части лейкоцитов, реагирующих на появление опухолевых клеток, происходит деметилирование сайта A(5mC)GC в зоне энхансера GH11J065646, что приводит к его активации [13].
Данные, представленные в данной работе, могут быть использованы для разработки ПЦР тест-системы, позволяющей исключить РМЖ на ранних стадиях. В этом случае вся работа по проведению анализа и исключению диагноза РМЖ состоит из следующих этапов:
- получение легкой фракции клеток крови,
- выделение ДНК из легкой фракции клеток крови,
- установление методом ПЦР в реальном времени концентрации геномной ДНК,
- определение методом GlaI-ПЦР анализа концентрации неметилированного сайта ACGC в положении хр11: 65647266 в препаратах ДНК из легкой фракции клеток крови и
- определение доли молекул ДНК, содержащих неметилированный сайт ACGC, выраженной в процентах от общего количества молекул ДНК.
Метод GlaI-ПЦР анализа не требует сложного и дорогостоящего оборудования и реактивов, а само исследование может проводиться в стандартной ПЦР-лаборатории в ходе ежегодных профилактических обследований и анализа крови.
В ДНК клеток крови, участвующих в иммунных процессах при РМЖ, вероятно, происходит изменение метилирования и других сайтов RCGY. Использование таких сайтов (вместе с ACGC сайтом в положении хр11: 65647266) для GlaI-ПЦР анализа позволит разработать ПЦР тест-системы с более высокой чувствительностью и специфичностью. Интерес также представляет изучение метилирования сайтов RCGY и, в частности, сайта ACGC в гене SIPA1, при других заболеваниях. В этом случае применение GlaI-ПЦР анализа для определения изменений в уровне метилирования сайтов RCGY в ДНК, выделяемой из легкой фракции клеток крови, позволит разработать диагностический метод для исключения таких болезней, аналогичный описанному в данной работе.
Патент работе находится в стадии оформления.
Литература
- World Cancer Report 2014 / B.W. Stewart, C.P. Wild (Eds.). Lyon, International Agency for Research on Cancer.
- Torre L.A., Bray F., Siegel R.L. et al. Global cancer statistics, 2012 // CA Cancer J. Clin. – – Vol. 65. – P. 87-108.
- Киселева Н.П., Киселев Ф.Л. Деметилирование ДНК и канцерогенез (обзор)// Биохимия — 2005.-Том 70.-Номер 7. Стр. 900 – 911.
- de Caseres I.I., Cairus P. Methylated DNA sequences for early cancer detection, molecular classification and chemotherapy response prediction // Clin. Transl. Oncol. – – Vol. 9. – P. 429-437.
- Handa V., Jeltsch A. Profound flanking sequence preference of Dnmt3a and Dnmt3b mammalian DNA methyltransferases shape the human epigenome // J. Mol. Biol. – – Vol. 348. – P. 1103-1112.
- Tarasova G.V., Nayakshina T.N., Degtyarev S.Kh. Substrate specificity of new methyl-directed DNA endonuclease GlaI // BMC Mol. Biol. – – Vol. 9:7.
- EV Dubinin, AG Akishev, MA Abdurashitov, SB Oleynikova, VL Sitko, and S Kh Degtyarev Real time GlaI-PCR assay of regulation regions of human genes HDAC4, RARB and URB1 // Research Journal of Pharmaceutical, Biological and Chemical Sciences, vol 7(2), p.p. 667-676 (2016).
- Набор для очистки ДНК из легкой фракции клеток крови // По состоянию на 28.12.2019 http://russia.sibenzyme.com/info1561.php
- В.А. Чернухин, М.А. Абдурашитов, В.Н. Томилов, Д.А. Гончар, С.Х. Дегтярев Сравнительный рестрикционный анализ хромосомной ДНК мыши in vitro и in silico // Вестник биотехнологии и физико-химической биологии имени Ю. А. Овчинникова, 2007, 3, №4, с. 19-27
- Инструкция к набору для GlaI ПЦР анализа // По состоянию на 28.12.2019 http://russia.sibenzyme.com/info7867.php
- Fishilevich S, Nudel R, Rappaport N, et al. GeneHancer: genome-wide integration of enhancers and target genes in GeneCards. Database (Oxford). 2017;2017:bax028
- Bell AC, Felsenfeld G (May 2000). «Methylation of a CTCF-dependent boundary controls imprinted expression of the Igf2 gene». Nature. 405 (6785): 482–5
- Kim S, Yu NK, Kaang BK. CTCF as a multifunctional protein in genome regulation and gene expression. Exp Mol Med. 2015;47(6):e166.